产品说明书
FAQ
COA
已发表文献
产品描述
Hieff NGS® Ultima Pro DNA Library Prep Kit for MGI® V2是针对MGI®高通量测序平台专业开发设计的新一代建库试剂盒。本产品采用高质量的酶学组成,在前一代建库试剂盒的基础上,改进了DNA片段末端修复和加A效率,同时改善了接头连接效率。本试剂盒采用新型的高保真酶,显著提高扩增均一性和保真性,可应用于常规动植物基因组、微生物基因组、FFPE、cfDNA、ChIP DNA等样本,助力获得优异的测序数据。

产品组分
|
组分编号 |
|
组分名称 |
产品编号/规格 |
||
|
13312ES08 |
13312ES24 |
13312ES96 |
|||
|
13312-A |
|
Endprep Buffer 2.0 |
48 μL |
144 μL |
576 μL |
|
13312-B |
|
Endprep Enzyme 2.0 |
32 μL |
96 μL |
384 μL |
|
13312-C |
|
Ligation Enhancer 2.0 |
240 μL |
720 μL |
3×960 μL |
|
13312-D |
|
Rapid T4 DNA Ligase 2.0 |
40 μL |
120 μL |
480 μL |
|
13312-E |
|
Canace® Pro Amplification Mix 2.0 |
200 μL |
600 μL |
3×800 μL |
|
13312-F |
|
Primer Mix for MGI® |
40 μL |
120 μL |
480 μL |
运输与保存方法
冰袋运输。所有组分-20 °C保存,有效期1年。
注意事项
一、关于操作
1. 为了您的安全和健康,请穿实验服并戴一次性手套操作。
2. 请于使用前将试剂盒各组分置于室温解冻。解冻后上下颠倒数次充分混匀,短暂离心后置于冰上待用。
3. 配制各步骤反应液时推荐使用移液器吹打混匀或轻轻振荡,剧烈振荡可能会造成文库产出下降。
4. 为避免样品交叉污染,推荐使用带滤芯的枪头,吸取不同样品时请更换枪头。
5. 推荐在带热盖的PCR仪中进行各步骤反应,使用前应预热PCR仪至反应温度附近。
6. PCR产物因操作不当极容易产生气溶胶污染,进而影响实验结果准确性。推荐将PCR反应体系配制区和PCR产物纯化检测区进行强制性的物理隔离;使用专用的移液器等设备;并定时对各实验区域进行清洁(使用0.5%次氯酸钠或10%漂白剂进行擦拭清理),以保证实验环境的洁净度。
7. 本产品仅作科研用途!
二、关于DNA片段化
1. 本试剂盒中兼容机械法及酶切法片段化的DNA。
2. 本试剂盒兼容范围为100 pg - 1000 ng Input DNA。应尽可能使用A260/A280 = 1.8-2.0的高质量Input DNA。表1中列举了将本试剂盒应用于常见应用中推荐的Input DNA量。
表1 常见应用中推荐Input DNA量
|
应用 |
样本类型 |
推荐Input DNA量 |
|
全基因组测序 |
复杂基因组 |
50 ng-1000 ng |
|
靶向捕获测序 |
复杂基因组 |
10 ng-1000 ng |
|
全基因组测序,靶向捕获测序 |
FFPE DNA |
50 ng-1000 ng |
|
全基因组测序,靶向捕获测序 |
cfDNA/ctDNA |
≥500 pg |
|
全基因组测序 |
微生物基因组 |
≥1 ng |
|
全基因组测序PCR-free测序 |
高质量DNA |
≥50 ng |
【注】:上表为使用高质量DNA时推荐的Input DNA量,当Input DNA质量较差或需要进行片段分选时,应适当上调使用量。
3. Input DNA特指投入末端修复/dA尾添加步骤中的DNA。
4. Input DNA制备过程中带入的高浓度金属离子螯合剂或其他盐,可能会影响末端修复/dA尾添加步骤反应效率,建议DNA片段化后进行磁珠纯化或分选。当使用机械法进行DNA片段化且产物不进行纯化或长度分选而直接建库时,请将DNA稀释在TE Buffer中进行片段化,请勿在灭菌超纯水中进行。
三、关于接头连接(Adapter Ligation)
1. 针对MGI® 高通量测序平台,Yeasen提供了Hieff NGS® Complete Adapter Kit for MGI®,Set 1~Set 3(Cat#13360 ~ Cat#13362),试剂盒中的接头浓度为10 μM;Hieff NGS® 384 CDI Primer for MGI®,Set 1~Set 2(Cat#13363 ~ Cat#13364),试剂盒中的接头浓度为10 μM;也可搭配Hieff NGS® Dual UMI UDB Adapter Kit for MGI®,Set 1~Set 2 (Cat#13367~Cat#13368)双端UMI UDB短接头,试剂盒中的接头浓度为10 μM。
2. Adapter的质量和使用浓度直接影响连接效率及文库产量。Adapter用量过高可能会产生较多Adapter Dimer;用量较低可能会影响连接效率及文库产量;使用Adapter时根据Input DNA量用TE Buffer进行相应稀释。表2列举了使用本试剂盒的不同Input DNA量推荐的Adapter稀释方法,表3列举了使用本公司Hieff NGS® Dual UMI UDB Adapter Kit for MGI®,Set 1~Set 2 (Cat#13367~Cat#13368)的不同Input DNA量推荐的UMI Adapter稀释方法。
表2 100 pg-1000 ng Input DNA推荐的Adapter使用浓度
|
Input DNA |
Adapter稀释倍数 |
浓度 |
|
<1 ng |
100倍稀释 |
0.1 μM |
|
1 ng ~ 10 ng |
50倍稀释 |
0.2 μM |
|
10 ng ~ 25 ng |
10倍稀释 |
1 μM |
|
25 ng ~ 100 ng |
5倍稀释 |
2 μM |
|
100 ng ~ 1000 ng |
2倍稀释 |
5 μM |
表3 100 pg-1000 ng Input DNA推荐的UMI Adapter使用浓度
|
Input DNA |
Adapter稀释倍数 |
浓度 |
|
5 ng ~ 25 ng |
50倍稀释 |
0.2 μM |
|
25 ng ~ 100 ng |
10倍稀释 |
1 μM |
|
100 ng ~ 1000 ng |
4倍稀释 |
2.5 μM |
四、关于磁珠纯化与分选 (Bead-based Clean Up and Size Selection)
1. DNA片段长度分选步骤可选择在末端修复/dA尾添加之前,或接头连接后,或文库扩增后进行。
2. 当Input DNA质量≥50 ng,您可选择在接头连接后分选;如Input DNA质量<50 ng,建议您在文库扩增后进行分选。
3. Ligation Enhancer中包含高浓度的PEG,会对双轮磁珠分选产生显著影响。因此,如在接头连接后进行长度分选,必须先进行纯化步骤,再进行双轮分选步骤;如在末端修复/dA尾添加之前或文库扩增后进行长度分选,可直接进行双轮磁珠分选步骤。
4. 磁珠使用前应先平衡至室温,否则会导致得率下降、分选效果不佳。
5. 磁珠每次使用前都应充分振荡混匀或使用移液器上下吹打充分混匀。
6. 转移上清时,请勿吸取磁珠,即使微量残留都将影响后续文库质量。
7. 磁珠漂洗使用的80%乙醇应现用现配,否则将影响回收效率。
8. 进行长度分选时,初始样品体积应尽量≥100 μL,不足时请用超纯水补齐。以防因样品体积太小导致移液误差增大。
9. 产物洗脱前应将磁珠置于室温干燥。干燥不充分容易造成无水乙醇残留影响后续反应;过分干燥又会导致磁珠开裂进而降低纯化得率。通常情况下,室温干燥3-5 min足以让磁珠充分干燥。
10. DNA纯化或长度分选产物如需保存,可使用TE Buffer洗脱,产物可于4 °C可保存1-2周,-20 °C可保存1个月。
五、关于文库扩增 (Library Amplification)
1. 是否需要进行文库扩增取决于Input DNA量、Adapter是否为完整长度、应用需要等因素。如使用非完整长度Adapter,必须进行这一步骤。如使用完整长度Adapter,当Input DNA<200 ng时,推荐进行文库扩增;当Input DNA≥200 ng或者不需要进行文库扩增时,可不进行文库扩增。
2. 文库扩增步骤需要严格控制扩增循环数。循环数不足,将导致文库产量低;循环数过多,又将导致文库偏好性增加、重复度增加、嵌合产物增加、扩增突变积累等多种不良后果。表4列举了使用本试剂盒,获得1 μg文库的推荐循环数。
表4 100 pg-1000 ng Input DNA获得1 μg产物扩增循环数推荐表
|
Input DNA |
1μg文库产量推荐PCR循环数 |
|
1000 ng |
2 - 4 |
|
500 ng |
2 - 4 |
|
250 ng |
4 - 6 |
|
100 ng |
5 - 7 |
|
50 ng |
7 - 9 |
|
10 ng |
9 - 11 |
|
5 ng |
10 - 12 |
|
1 ng |
12 - 14 |
|
100 pg |
16 - 18 |
【注】:
1.表4为使用200 bp左右的高质量Input DNA测试的循环数参数。FFPE DNA质量差异较大,当DNA质量较差或文库长度较长时,需适当提高循环数以获取足量文库。
2.如果建库过程中需要进行过片段分选,推荐较高循环数进行Library Amplification;反之则参照较低循环数即可。
3.如果使用了不完整的接头,需要扩增至少2个循环,形成完整的接头。
六、关于文库质检 (Library Quality Analysis)
1. 通常情况下,构建好的文库可通过长度分布检测和浓度检测来进行质量评价。
2. 文库浓度检测可使用:基于双链DNA荧光染料的方法,如Qubit®、PicoGreen®等;基于qPCR绝对定量的方法。
3. 文库浓度检测不可使用:基于光谱检测的方法,如NanoDrop®等。
4. 推荐使用qPCR方法进行文库浓度检测:Qubit®、PicoGreen®等基于双链DNA荧光染料的浓度测定方法时,无法有效区分单端连接Adapter的产物、两端均未连接Adapter的产物以及其他不完整双链结构产物;qPCR绝对定量基于PCR扩增原理,仅定量样品中两端Adapter完整的文库(即可测序的文库),可排除单端或双端都不连接Adapter的不可测序文库的干扰。
5. 文库长度分布检测,可通过Agilent Bioanalyzer 2100等基于毛细管电泳或微控流原理的设备进行检测。
使用方法
一、自备材料
1. 纯化磁珠:Cat#12601,Hieff NGS® DNA Selection Beads或Cat#A63880,AMPure XP Beads或其他等效产品。
2. DNA质控:Agilent Technologies 2100 Bioanalyzer或其他等效产品。
3. DNA Adapter:可选Yeasen 提供的Hieff NGS® Complete Adapter Kit for MGI®,Set 1~Set 3(Cat#13360 ~ Cat#13362);Hieff NGS® 384 CDI Primer for MGI®,Set 1~Set 2(Cat#13363 ~ Cat#13364);Hieff NGS® Dual UMI UDB Adapter Kit for MGI®,Set 1~Set 2 (Cat#13367~Cat#13368)DNA 文库构建专用配套试剂盒,接头详细介绍信息参考上面注意事项中的第三部分“关于接头连接”。
4. 其他材料:无水乙醇、灭菌超纯水、TE Buffer (10 mM Tris-HCl,pH 8.0-8.5+1 mM EDTA)、低吸附EP管、PCR管、磁力架、PCR仪等。
二、操作流程
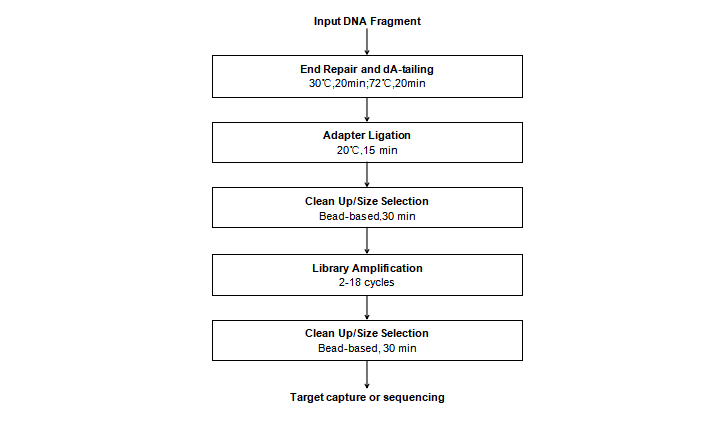
图1 Hieff NGS® Ultima Pro DNA Library Prep Kit for MGI® V2操作流程
三、操作步骤
3.1 末端修复/dA尾添加 (End Repair/dA-Taling)
该步骤将片段化后的Input DNA末端补平,并进行5’端磷酸化和3’端加dA尾。
1. 将表4中各试剂解冻后,颠倒混匀,置于冰上备用。
2. 于无菌PCR管中配制表5所示反应体系。
表5 末端修复/dA尾添加PCR反应体系
|
名称 |
体积 (μL) |
|
Fragmented DNA |
x |
|
Endprep Buffer 2.0 |
6 |
|
Endprep Enzyme 2.0 |
4 |
|
ddH2O |
Up to 60 |
3. 使用移液器轻轻吹打或振荡混匀,并短暂离心将反应液离心至管底。
4. 将上述PCR管置于PCR仪,设置表6所示反应程序,进行末端修复/dA尾添加反应。
表6 末端修复/dA尾添加PCR反应程序
|
温度 |
时间 |
|
热盖105 °C |
On |
|
30 °C |
20 min |
|
72 °C |
20 min |
|
4 °C |
Hold |
3.2 接头连接 (Adapter Ligation)
该步骤将3.1步骤的产物末端,连接特定的MGI®接头。
1. 根据Input DNA量按表2/表3稀释Adapter至合适浓度。
2. 将表7中各试剂解冻后颠倒混匀,置于冰上备用。
3. 于3.1步骤PCR管中配制表7所示反应体系。
表7 Adapter Ligation PCR体系
|
名称 |
体积 (μL) |
|
dA-tailed DNA(3.1步骤产物) |
60 |
|
Ligation Enhancer 2.0 |
30* |
|
DNA Adapter |
5** |
|
Rapid T4 DNA Ligase 2.0 |
5 |
【注】:*Ligation Enhancer比较粘稠,请上下颠倒、振荡,充分混匀并瞬时后离心使用。
**本公司接头浓度与常规商业化试剂盒一致,皆为10 μM。请根据注意事项三中的提示,对接头进行稀释,加水补齐,使接头体积为5 μL。
4. 使用移液器轻轻吹打或振荡混匀,并短暂离心将反应液收集至管底。
5. 将PCR管置于PCR仪中,设置表8所示反应程序,进行接头连接反应:
表8 Adapter Ligation PCR反应程序
|
温度 |
时间 |
|
热盖 |
Off |
|
20 °C |
15 min |
|
4 °C |
Hold |
【注】:当Input DNA量较低,实验效果不理想时,可尝试将连接时间延长一倍。
3.3 连接产物磁珠纯化 (Post-Ligation Clean Up)
该步骤使用磁珠对3.2步骤的产物进行直接纯化或分选。纯化可除去未连接的Adapter或Adapter Dimer等无效产物。直接纯化步骤参考3.3.1,分选步骤参考3.3.2。
3.3.1 纯化操作步骤:
1. 准备工作:将Hieff NGS® DNA Selection Beads磁珠由冰箱中取出,室温平衡至少30 min。配制80%乙醇。
2. 涡旋振荡或充分颠倒磁珠以保证充分混匀。
3. 吸取60 μL Hieff NGS® DNA Selection Beads (0.6×,Beads:DNA=0.6:1)至Adapter Ligation产物中,涡旋混匀或移液器吹打10次混匀,室温孵育5 min。
4. 将PCR管短暂离心并置于磁力架中分离磁珠和液体,待溶液澄清后(约5 min),小心移除上清。
5. 保持PCR管始终置于磁力架中,加入200 μL新鲜配制的80%乙醇漂洗磁珠,室温孵育30 sec后,小心移除上清。
6. 重复步骤5,总计漂洗两次。
7. 保持PCR管始终置于磁力架中,开盖空气干燥磁珠至刚刚出现龟裂(不超过5 min)。
8. 将PCR管从磁力架中取出,进行洗脱:
1)如产物无需进行片段分选,直接加入21 μL ddH2O,涡旋振荡或使用移液器轻轻吹打至充分混匀,室温静置5 min。将PCR管短暂离心并置于磁力架中静置,待溶液澄清后(约5 min),小心移取20 μL上清至新PCR管中,切勿触碰磁珠。
【注】:如纯化产物如需保存,可使用TE Buffer洗脱。
2)如产物需进行双轮分选,加入102 μL ddH2O,涡旋振荡或使用移液器轻轻吹打至充分混匀,室温静置5 min。将PCR管短暂离心并置于磁力架中静置,待溶液澄清后(约5 min),小心移取100 μL上清至新PCR管中,切勿触碰磁珠。
【注】:如纯化产物如需保存,可使用TE Buffer洗脱。
3.3.2 双轮分选操作步骤:
1. 准备工作:将Hieff NGS® DNA Selection Beads磁珠由冰箱中取出,室温平衡约30 min。配制80%乙醇。
2. 请涡旋振荡或充分颠倒磁珠以保证混匀。
3. 根据DNA片段长度要求,参考表9向上述100 μL DNA上清中加入第一轮分选磁珠,涡旋或移液器吹打10次混匀。
表9 磁珠文库分选推荐比例
|
DNA文库插入片段大小 |
150 - 250 bp |
200-300 bp |
300-400 bp |
|
DNA文库大小 |
230 - 330 bp |
280-380bp |
380-480bp |
|
第一轮体积比(Beads:DNA) |
0.78× |
0.68× |
0.58× |
|
第二轮体积比(Beads:DNA) |
0.20× |
0.20× |
0.20× |
【注】:表中“×”表示样品DNA体积。如文库插入片段长度为250 bp,样品DNA体积为100 μL,则第一轮分选磁珠使用体积为0.70×100 μL=70 μL;第二轮分选磁珠使用体积为0.20×100 μL=20 μL;表中所推荐比例是针对于Adapter Ligated Insert DNA (Post Ligation),如果用户在接头连接前进行分选,请采用Hieff NGS® DNA Selection Beads (Cat#12601)说明书中推荐的比例。
4. 室温孵育5 min。
5. 将PCR管短暂离心并置于磁力架中,待溶液澄清后(约5 min),小心转移上清到干净的离心管中。
6. 参考表8向上清中加入第二轮分选磁珠。
7. 涡旋混匀或移液器吹打10次混匀,室温静置5 min。
8. 将PCR管短暂离心并置于磁力架中,待溶液澄清后(约5 min),小心移除上清。
9. 保持PCR管始终处于磁力架中,加入200 μL新鲜配制的80%乙醇漂洗磁珠,室温孵育30 sec,小心移除上清。
10. 重复步骤9。
11. 保持PCR管始终处于磁力架中,开盖干燥磁珠至刚刚出现龟裂(约5 min)。
12. 将PCR管从磁力架中取出,加入适量21 μL ddH2O,涡旋振荡或使用移液器轻轻吹打充分混匀,室温静置5 min。
13. 将PCR管短暂离心并置于磁力架中分离磁珠和液体。待溶液澄清后(约5 min),小心转移20 μL上清至干净的管中。
3.4 文库扩增 (Library Amplification)
该步骤将对纯化或长度分选后的接头连接产物进行PCR扩增富集。
1. 将表10中试剂解冻后颠倒混匀,置于冰上备用。
2. 于无菌PCR管中配制表10所示反应体系。
表10 PCR扩增反应体系
|
名称 |
体积 (μL) |
|
Adapter Ligated DNA(3.3步骤产物) |
20 |
|
Canace® Pro Amplification Mix 2.0 |
25 |
|
Primer Mix for MGI® |
5 |
【注】:*如果使用的是华大智造提供的接头,关于其使用要求,请详见华大智造“关于 Adapter 使用”有关说明或咨询本公司。如果使用的是Yeasen提供的完整接头(Cat # 13360 ~ Cat # 13362),使用试剂盒中的Primer Mix for MGI®进行扩增;如果使用了不完整的接头(Cat # 13363 ~ Cat# 13364),请参照上述试剂盒说明书,使用其中配备的UDB Primer进行扩增。如果使用的是双端UMI UDB不完整接头(Cat # 13367~ Cat# 13368),请参照上述试剂盒说明书,使用其中配备的UDB Primer进行扩增。
3. 使用移液器轻轻吹打或振荡混匀,并短暂离心将反应液收集至管底。
4. 将PCR管置于PCR仪中,设置表11所示反应程序,进行PCR扩增。
表11 PCR扩增反应程序
|
温度 |
时间 |
循环数 |
|
98 °C |
1 min |
1 |
|
98 °C |
10 sec |
参照注意事项中表4 |
|
60 °C |
30 sec |
|
|
72 °C |
30 sec |
|
|
72 °C |
5 min |
1 |
|
4 °C |
Hold |
- |
3.5 扩增产物磁珠纯化或分选 (Post Amplification Clean Up/Size Selection)
同3.3.1步骤中纯化操作步骤。使用Hieff NGS® DNA Selection Beads (0.9×,Beads:DNA=0.9:1)纯化文库扩增产物。
如需分选,操作方法同3.3.2双轮分选步骤(纯化步骤可省略)。
3.6 文库质量控制
通常情况下,构建好的文库可通过浓度检测和长度分布检测来进行质量评价,具体请参见注意事项六。
HB220928












