干货|你对DNase I“全能选手”了解多少?
“
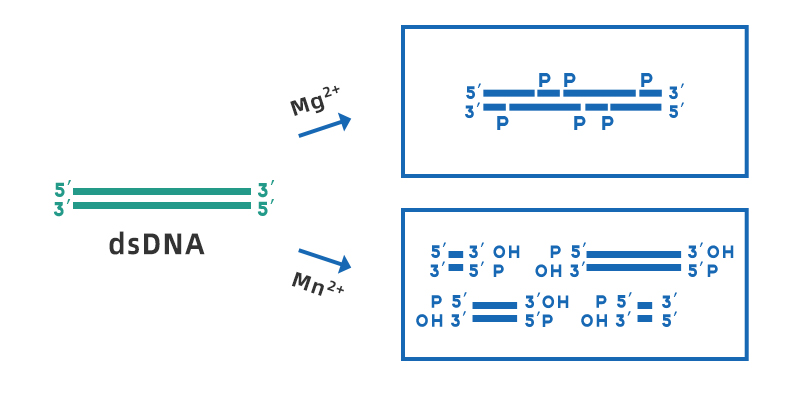
RNA提取或反转录前去除gDNA
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
“
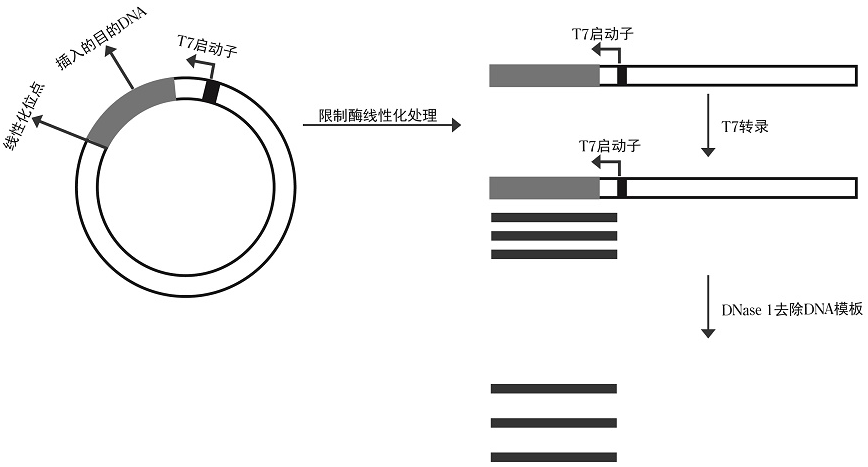
体外转录去除模板DNA
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
“
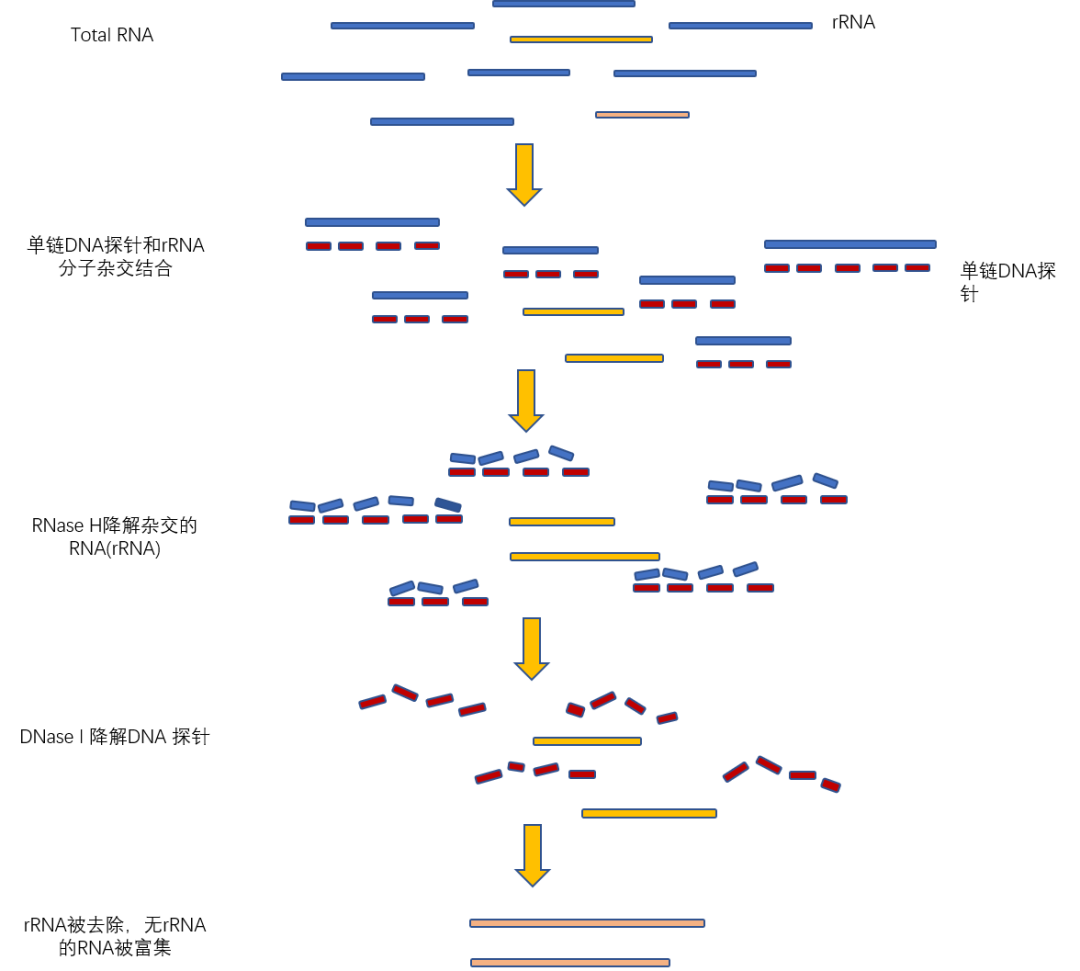
rRNA去除:常应用于RNA建库测序
操作步骤
1.提取Total RNA;
2.单链DNA探针和rRNA分子杂交结合(注:需要设计与合成rRNA 特异性单链 DNA 探针);
3.RNase H降解杂交的rRNA;
4.DNase I降解DNA 探针;
5.rRNA被成功去除,剩下非rRNA的RNA模板。
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
“
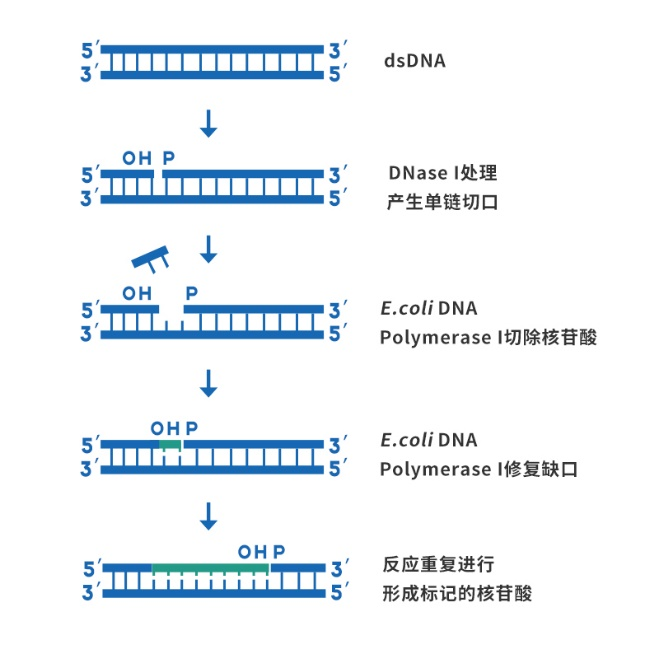
缺口平移法进行DNA标记
主要原理如下:
1.先用适宜浓度的DNase I在待标记的双链DNA的每一条链上产生若干个单链缺口,缺口处形成3’羟基末端。
2.再用E.coli DNA Polymerase I的5’→3’外切酶活性从缺口处5’端切除一个核苷酸,同时E.coli DNA Polymerase I的5’→3’聚合酶活性将一个带标记的核苷酸引入到缺口的3'端,以修补缺口,随着缺口在DNA链上的移动,标记的核苷酸就掺入到新合成的DNA链中。
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
“
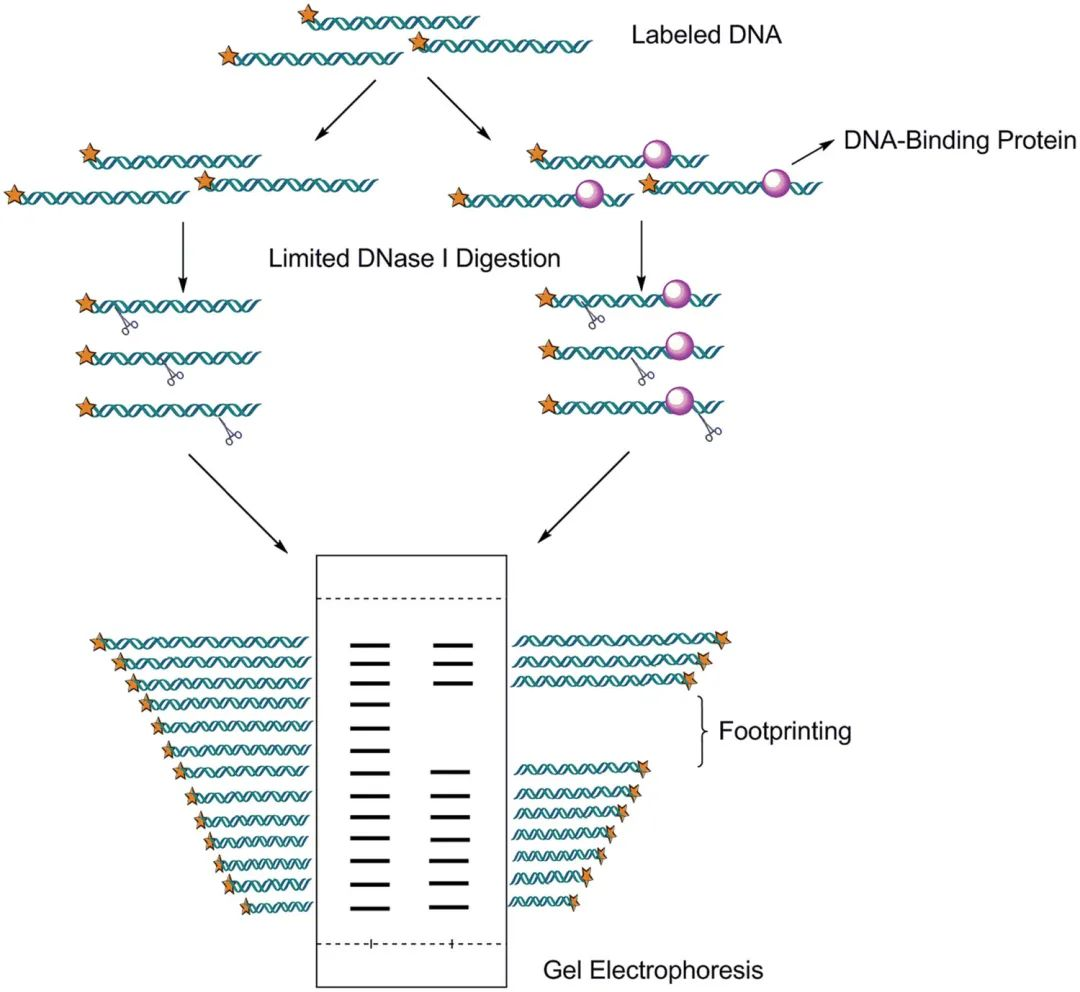
DNase I 足迹法分析实验
实验大致步骤如下:
1.将待检双链DNA分子进行单链末端标记。
2.将蛋白质和DNA混合后,加入适量的DNase I进行酶切,形成不同长度的DNA片段。该过程需要控制酶的用量,最好保证相邻的DNA片段只相差一个核苷酸,并列设置未加蛋白质的对照。
3.从DNA上除去蛋白质,将变性的DNA用PAGE电泳分离,放射自显影,与对照组相比后解读出足迹部位的核苷酸序列。
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
|
